TEM?116型ESBL天然酶与重组酶的动力学特性研究
作者:曾贤铭 陈秀枢 王震 吕建新 楼永良 孙长贵 陆永绥
【摘要】 目的 研究TEM?116型ESBL天然酶与重组酶的动力学特性,并比较它们的差异。方法 采用紫外分光光度法检测酶促抗生素水解反应,以Lee?Wilson改良双倒数方程数据处理法进行数据处理,测定天然酶与重组酶的Km、Vmax及kcat。观察温度和pH对酶促反应的影响。结果 以Lee?Wilson改良双倒数方程数据处理法进行数据处理方便而准确地测定了天然酶与重组酶的Km与Vmax并出kcat。温度和pH对天然酶与重组酶酶促反应效应相似。天然酶与重组酶最优先的底物均为头孢哌酮,其次是头孢氨苄;对氨苄西林、阿莫西林、青霉素和哌拉西林有最高的催化效率。结论 天然酶与重组酶的动力学参数无显著差异。
【关键词】 动力学 β内酰胺酶 重组蛋白 β内酰胺类抗生素
Kinetic characteristics of native and recombinant TEM?116 beta?lactamases
ABSTRACT Objective To investigate and compare the kinetic characteristics of native and recombinant TEM?116 beta?lactamases. Methods Hydrolysis reactions of beta?lactam antibiotics were detected by ultraviolet photometry. Data was processed according to Lee and Wilson′s improved double?reciprocal equation. Kinetic parameters of native and recombinant TEM?116 beta?lactamases, including Km, Vmax and kcat, were determined. Effects of temperature and pH on enzymatic reaction were observed. Results Michaeles constant (Km) and maximal velocity (Vmax) were obtained by means of Lee and Wilson′s improved double?reciprocal equation, and the catalytic constant (kcat) was calculated. There were similar pH or temperature effects on either native or recombinant beta?lactamases. The most preferential substrate for both native and recombinant TEM?116 beta?lactamases is cefoperazone and followed by the next cephalexin. Among the highest catalytic efficiency are ampicillin, amoxicillin, penicillin and piperacillin. Conclusion There is no difference of kinetic characteristics between native and recombinant TEM?116 beta?lactamases.
KEY WORDS Kinetics; Beta?lactamases; Recombinant proteins; Beta?lactam antibiotics
ESBLs的产生机制是细菌在抗生素选择压力下,由TEM?1或TEM?2型酶的活性中心发生一个或数个位点的突变,导致底物谱的超广谱化[1]。2002年首先分离自Klebsiella pneumonia和Escherichia coli临床株的TEM?116型超广谱β?内酰胺酶(extended?spectrum?beta?lactamases,ESBL)是病原菌产生的一种耐药酶,能够催化水解青霉素类、第一~三代头孢菌素等β?内酰胺抗生素的内酰胺环,使之失去抗菌活性。TEM型ESBLs是在亚洲地区具有流行趋势的超广谱酶,与TEM?1相比,它在第84位点由Ile置换Val,在184位点由Val置换Ala,由于这两个氨基酸位点的突变,导致它对青霉素类药物保持高催化效率的同时,还能够水解绝大部分的第一~三代头孢菌素[2,3]。该酶属于Bush功能分类2be群,Ambler结构分类A类[4,5]。
基因水平的分子生物学特征和以底物谱为基础的酶动力学特性是研究新型ESBLs的两个重要途径,也是新型β?内酰胺药物开发和酶抑制剂研究的标志性指标[6,7]。由于高纯度酶的获取十分困难,我们认为以往大多以部分纯化或粗制酶为材料所进行的有关动力学研究结果在间的可比性和实际引用中的参考性等方面存在一定缺陷[8]。在动力学特征研究中,准确和精密的Km和kcat是最重要的动力学参数[9,10],前者表示酶与底物的亲和能力 ,后者是酶完全被底物饱和时单位时间内每个酶活性中心所能催化底物转变为产物的分子数,又称酶的催化常数(catalytic constant)。为此,我们以高纯度TEM?116型天然酶和重组酶为材料,对16种β?内酰胺药物进行动力学特性和其它生物化学参数进行比较性研究,报告如下。
1 材料与方法
1.1 仪器与器材
发酵罐(BIOSTAT ED 10L,BBI,德国);AKTA蛋白质分离纯化系统(GE Healthcare?formerly AmershamBiosciences,美国);十万分之一天平(Shimadzu,日本);UV?2201/Visrecording(Shima?dzu,日本);CEQTm8800基因测序系统(Beckman Coulter);测定等电点的预制IEF polyacrylamide gel(Bio?Rad,Hercules,CA);Sephacryl S?100(XK 50/100)柱;Sephadex G25(XK 50/100)柱。
1.2 抗生素与试剂
氨曲南(aztreonam,AZ)购自上海施贵宝制药有限公司;头孢西丁(cefoxitin,CFX)海南海药股份公司产品;亚胺培南(imipenem,IMP)杭州默沙东公司生产;呈色头孢菌素头孢硝噻吩(nitrocefin)购自Oxoid(Basingstoke,英国)。以下抗生素均为药品生物制品检定所化学对照品:头孢氨苄(cephalexin,CEL);头孢羟氨苄(cefadroxil,CFR);头孢拉定(cephradine,CED);头孢唑林(cefazolin,CEZ);头孢呋新(cefuroxime,CXM);头孢哌酮(cefoperazone,CPZ);头孢噻肟(cefotaxime,CTX);头孢曲松(ceftriaxone,CRO);头孢他啶(ceftazidime,CAZ);氨苄西林(ampicillin,ABPC);阿莫西林(amoxicillin,AMPC);哌拉西林(piperacillin,PIPC);苯唑西林(oxacillin,OXA);氯唑西林(cloxacillin,CXC);青霉素(penicillin,PC);克拉维酸(clavulanic acid,CA)。其它化学试剂均为分析纯。
1.3 菌株与高纯度TEM?116型天然酶和重组酶
高产TEM?116型ESBL的Escherichia coli临床株(E.coli WZO2)分离自尿路感染的尿样本,经API 20E系统(Bio?Merieux,法国)鉴定。工程菌的重组、测序与鉴定、天然菌和重组菌的发酵、酶蛋白的分离与纯化均由本基金项目另一课题实施。其主要步骤为:单个菌落接种于100ml含30μg/ml的LB肉汤中,37℃摇床培养8~12h(200r/min)后,取其70ml转种于含30μg/ml的7.0L LB肉汤中,发酵罐内37℃培养至A600 1.7~1.8时,加入诱导剂并在30℃继续孵育6~8h,然后,浓集菌体经超声裂解、包涵体(重组菌形成,天然菌无)复性、溶解后,在AKTA蛋白质纯化系统,溶解液通过预平衡的Sephacryl S?100柱,再通过Sephadex G25柱脱盐,用头孢硝噻吩为底物检测确认,收集高浓度酶活性组分,经Centriprep?10滤膜(Amicon,Lexington,Mass.)过滤浓缩后,低温冰冻干燥、分装后存于-20℃备用,天然酶每瓶0.372mg蛋白,测定前以0.01mol/L、pH7.0的磷酸盐缓冲液(PBS)复溶至890μl;重组酶每瓶0.418mg蛋白,以上述PBS复溶至1000μl。活性组分在AKTA系统HPLC,280nm处监测为单一峰,经聚丙烯酰胺凝胶等电聚焦电泳后,以头孢硝噻吩呈色为单一条带,SDS?PAGE考马斯亮蓝染色鉴定,结果均证明其纯度≥95%。同时,检测证明TEM?116天然酶的分子量为28.8ku、pI为5.4,与文献报告一致[2];重组酶是含有6×His的融合蛋白,分子量为29.8ku,pI为5.5。
1.4 动力学研究
(1)测定波长选定 抗生素和酶蛋白均以0.01mol/L、pH7.0的PBS溶解,设:参比管(PBS),空白管(抗生素溶液,各种药物的最高浓度由初试验确定,原则是其最大吸收在0.6~0.8?),试验管(抗生素溶液+酶溶液)。各管均于37℃孵育0.5~4h,以PBS为参比,(37±0.3)℃条件下,在200~400nm区间进行扫描,将空白管和试验管之间吸光度差值最大的波长,确定为本实验的测定波长。
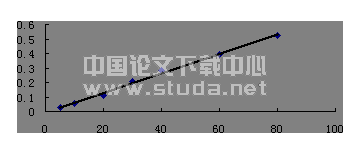
(2)反应速度与底物浓度 根据Lee?Wilson的改良双倒数方程标准,连续扫描检测紫外区测定波长下吸光度的动态变化,并以吸光度对时间自动作图,选取自起始点开始10~12个连续的时间段,各时间段的平均反应速度与平均底物浓度,作为该时间段中间时刻点的反应速度与底物浓度。
(3)动力学特征参数测定 对各抗生素均取10~12个时刻点的反应速度与底物浓度,用SPSS统计学软件根据方程作图,得回归方程,求取Km与Vmax(经两次实验测定取平均值)。根据反应体系中加入酶量以及Km、Vmax计算kcat及其它衍生参数。
1.5 其它催化特性
(1)温度对酶促反应的影响 以200μmol/L的头孢哌酮分别在30、35、37及40℃测定酶反应速度,观察温度对酶反应速度的影响。
(2)pH对酶促反应的影响 以pH6.5、7.0和7.4的PBS于临用前配制200μmol/L的头孢哌酮溶液,经37℃预温并加入酶液,观察不同pH对酶促反应速度的影响。
(3)克拉维酸对酶促反应的抑制作用 200μmol/L的头孢哌酮在pH7.0、37℃条件下,测定酶反应速度,并加入不同浓度克拉维酸观察反应速度的变化。
2 结果
2.1 天然酶和重组酶动力学参数
在完全相同的实验条件下,对TEM?116型天然酶和重组酶的动力学测定结果分别见Tab.1和Tab.2。实验结果显示TEM?116型β?内酰胺酶对亚胺培南与头孢西丁没有水解作用,该结果与报告的对上述两种药物MIC分别为0.125~0.25和2~4μg/ml基本一致[2]。
2.2 天然酶与重组酶的动力学参数比较用SPSS统计学软件对Km、kcat、kcat/Km三项参数 进行配对t检验,结果显示,天然酶与重组酶Km(t=1.334,P=0.202)、kcat(t=1.362,P=0.193)、kcat/Km(t=1.479,P=0.160)无显著性差异。
2.3 温度和pH对酶促反应的影响
以200μmol/L的头孢哌酮为底物,分别观察温度和pH对酶促反应的影响,以37℃和pH7.0条件下的酶活力为100%计,实验结果表明,天然酶和重组酶具有对温度的较好稳定性;偏酸环境对酶具有显著的抑制作用,结果见Tab.3。
2.4 克拉维酸对酶促反应的抑制作用
天然酶和重组酶50%活力受抑制的克拉维酸浓度分别为7.9和9.1μmol/L。
3 讨论
在测定β?内酰胺酶的动力学特性时,由于β?内酰胺抗生素的水解产物在紫外区吸光度比原底物的吸光度低得多,如果直接测定水解产物生成量,实验因受底物吸光度的严重干扰而难以进行。所以,测定底物的减少量是唯一有效的方法。但是,目前经常应用的根据米氏微分方程重排所得到的线性方程作图求取Km与Vmax的方法主要有Lineweaver?Burk法、Eadie?Hofstee法、Eisenthal?Cornish?Bowden法和Hanes?Woolf法等,这些方法均需测定反应的初速度,并要求底物被转化的量小于5%才能够减少实验误差。所以,这些方法不适应于对β?内酰胺酶的动力学特征测定。Lee和Wilson根据米氏方程可变形为积分形式,推导出改良的双倒数作图法处理实验数据,该方法优点是即使底物分解30%,所引入的误差也仅1%,相比之下,上述Lineweaver?Burk法等四种方法在底物被转化10%时,所导致的误差可高达6%[11,12]。该方法除取消了5%的底物分解限制外,还要求对反应进行连续检测,并选取多个连续的时间段,计算各时间段的平均反应速度与平均底物浓度作为该时间段中间时刻的反应速度与底物浓度,这些实验条件特点对测定吸光度变化很小的青霉素类的水解特别重要。
另一个值得讨论的问题是绝大部分β?内酰胺抗生素与其水解产物均仅在紫外区有特征吸收,所以,使用未经提纯的粗制酶(菌体破碎后高速离心的上清液或者纯度不高的酶蛋白)测定其动力学参数时,因其中含有大量杂蛋白等,在紫外区也有较强的吸收而干扰吸光度的准确测定,尤其对需要在较短波长下测定的青霉素类更严重。由于测定酶动力学参数要求实验条件具备较高的准确度和精密度,因此,我们认为既往许多研究者使用粗制酶进行动力学参数测定的作法是不合适的。
本研究使用纯度高达95% β?内酰胺酶进行酶动力学实验,既有利于获取准确的实验数据,也是测定kcat的必要条件,能够准确地计算加入反应体系中的酶分子摩尔数。同时,我们以Km、kcat和kcat/Km三个参数比较全面的评价了天然酶与重组酶的动力学特征,并证明两者之间在催化动力学方面没有显著差异。在本研究中,TEM?116酶对头孢哌酮亲和力最高,说明头孢哌酮是该酶的最优先的底物,其次是头孢氨苄。用催化常数评价,结论是对氨苄西林、阿莫西林、青霉素和哌拉西林远高于其它头孢类药物,表明在底物饱和的情况下,对青霉素类抗生素具有较快的转化率;而头孢菌素中则对头孢唑林具有较高的催化效率,但仍远小于氨苄西林。就综合效率参数kcat/Km而言,青霉素类抗生素有最高的催化效率。这些结果对于抗生素耐药性研究、内感染控制、临床抗菌药物的选择等均具有一定的意义。
【参考文献】
[1] Bradford P A. Extended?spectrum β?lactamases in the 21st century: Characterization, epidemiology, and detection of this important resistance threat [J]. Clin Microbiol Rev,2001,14(4):933
[2] Jeong S H, Bae I K, Lee J H, et al. Molecular characterization of extended?spectrum beta?lactamases produced by clinical isolates of Klebsiella pneumoniae and Escherichia coli from a Korean nationwide survey [J]. J Clin Microbiol,2004,42(7):2902
[3] Vignoli R, Varela G, Mota M I, et al. Enteropathogenic Escherichia coli strains carrying genes encoding the PER?2 and TEM?116 extended?spectrum beta?lactamases isolated from children with diarrhea in Uruguay [J]. J Clin Microbiol,2005,43(6):2940
[4] Bush K, Jacoby G A, Medeiros A A. A functional classification scheme for β?lactamase and its correlation with molecular structure [J]. Antimicrob Agents Chemother,1995,39(6):1211
[5] Ambler R P. The structure of beta?lactamases [J]. Philos Trans R Soc Lond B Biol Sci,1980,289(1036):321
[6] Gary W, Huang W, Timothy P. Binding properties of a peptide derived from β?lactamase inhibitory protein [J]. Antimicrob Agents Chemother,2001,45(2):3279
[7] Yribarren A, Thomas D, Friboulet A, et al. Selection of peptides inhibiting a beta?lactamase?like activity [J]. Eur J Biochem,2003,270(13):2789
[8] Silva J, Aguilar C, Ayala G, et al. TLA?1: a new plasmid?mediated extended?spectrum β?lactamase from Escherichia coli [J]. Antimicrob Agents Chemother,2000,44(4):997
[9] Poirel L, Mammeri H, Nordmann P, et al. TEM?121, a novel complex mutant of TEM?type β?lactamase from Enterobacter aerogenes [J]. Antimicrob Agents Chemother,2004,48(12):4528
[10] Alba J, Ishii Y, Thomson K, et al. Kinetics study of KPC?3, a plasmid?encoded class A carbapenem?hydrolyzing β?lactamase [J]. Antimicrob Agents Chemother,2005,49(11):4760
[11] Zou G L, Zhu R F. Enzymology(酶学)[M]. 1st edition. Wuhan: Wuhan university press,1997:76
[12] Lee H J, Wilson I B. Enzymic parameters: measurement of V and Km [J]. Biochim Biophy Acta,1971,242(3):519