红曲菌株的RAPD多态性分析
【摘要】 [目的]研究红曲分离株的遗传多样性和亲缘关系,为种质鉴定、保护和利用提供。[方法]用随机引物对10个红曲菌株进行RAPD分析,从中筛选出63特征性好,多态性高的RAPD图谱,用NTSYS?PC?2.1软件进行同一性和差异性分析并根据遗传距离构建系统进化树。[结果]红曲分离株间的同一性平均73.32%,表明它们的遗传背景具有很大的相似性;RAPD聚类结果与菌株的形态差异相关,表明RAPD分子标记进行菌株鉴别与传统形态分类鉴别结果基本一致,鉴别能力较强。 [结论]基于RAPD多态性的遗传分析能从分子水平上揭示红曲菌的遗传背景差异,为分类鉴定、种质起源和系统进化提供辅助手段和技术依据。
【关键词】 红曲菌;RAPD分析;遗传同一性;系统进化树
Abstract: [Objective] To study the genetic diversity and relative relationship of different Monascus trains to provide reference for classification and protection of germ plasm resources.[Methods] Comparing the results of the random amplified polymorphic DNA (RAPD) fingerprints derived from 10 cultivated strains of Monascus, 63 RAPD electrophoresis atlases were selected to calculate the genetic identity and divergence among them by NTSYS?PC?2.1 software.And then phylogenetic tree of Monascus strains was conceived according to their genetic distance by clustering method.[Results] It was suggested that the comparability of genetic backgrounds was plenty because of 73.32% average identity of Monascus strains.The results of RAPD analysis were consistent with that of morphologic study, so the RAPD molecular marker technology is an effective way to identify Monascus strains.[Conclusion] RAPD analysis can reveal the differentia of genetic backgrounds of Monascus strains, and it could be applied widely in classification and identification, germ plasm origin and evolution.
Key words: Monascus; RAPD analysis; genetic identity; phylogenetic tree
红曲是一味在《本草纲目》、《医林纂要》等都有记载的天然佳品。长期以来,对红曲菌分类鉴定均根据其形态特征和生特性 [1?4]。由于红曲菌属下分类的形态、生化指标均受培养基质、温度等环境条件影响,表现出较大差异性,加上有些种界限不明确,使红曲菌的命名和分类在学术上颇多争议[5]。
DNA分子在物种鉴别分类和筛选上比形态学、血清学、化学指纹图谱等更准确,目前已有限制性酶酶切片段长度多态性(RFLP),随机扩增多态DNA(RAPD),串联重复序列(SSR)等[6]直接在DNA水平上进行遗传分析的实验方法。由于红曲菌的分子生物学研究起步较晚,基因组序列相关信息尚不清楚,限制了常规分子生物学方法的使用。RAPD标记技术不需要预先知道DNA序列信息,对DNA质与量要求不高,引物无种属界限[7]等优点使其成为研究红曲菌株鉴别、遗传分析的首选。
1 材料和方法
1.1 实验材料
1.1.1 供试菌株及培养基:供试红曲菌株编号1~10依次为AS 3.554、AS 3.972、B、F、J、M?2、P、S、ZW?5、古田,其中F为Monascus ruber,余为Monascus anka.。B、F、J、P、S由浙江中医药大学肿瘤研究室保存,AS 3.554、AS 3.972、M?2、ZW?5、古田购自浙江省微生物研究所,AS 3.554、AS 3.972为普通微生物菌种保藏中心保存菌株。MEA(malt extract agar)[6]培养基。
1.1.2 主要试剂及随机引物:主要分子生物学试剂购自杭州博日科技有限公司及宝生物工程(大连)有限公司,RAPD分析所用1O碱基随机引物S251?S350、S2001?S2050购自上海生工生物技术公司,编号及核苷酸序列见上海生工生物技术公司网页。
1.2 实验方法
1.2.1 红曲基因组DNA的提取:红曲菌体基因组DNA的提取采用CTAB法[8]进行。
1.2.2 RAPD反应体系:RAPD反应体系为1×PCR Bufer,dNTPs 1mmol/L,Taq酶1.2U,随机引物0.2μmol/L,模板DNA 20ng,反应总体积为20μL。
1.2.3 RAPD反应参数:扩增反应在梯度PCR扩增仪上进行,94℃预变性6min,进入92℃变性40s、36℃退火40s、72℃延伸2min的35个循环,最后72℃补平7min,4℃终止反应。
1.2.4 RAPD多态性分析:根据片段大小排列并记录,条带有计为“1”;条带无计为“0”,构建原始数据0?1矩阵,用NTSYS?PC?2.1软件出同一性和差异性,并用clustering中的UPGMA聚类方法构建系统进化树;用Edit file生成遗传同一性和差异性表。
2 结果
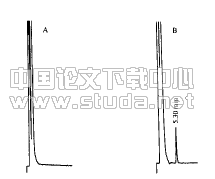
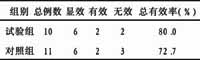
2. 1 红曲菌的RAPD电泳图谱:用150条随机引物扩增10株红曲菌基因组DNA,筛选出条带多,特征性好,多态性高的63个电泳图谱作为RAPD分析依据。不同红曲分离株RAPD扩增产物有3~9条带,多集中在300~1500bp,其中主条带2~4条,次带丰富,各菌株间既有相同条带又有差异条带,如图1。
2.2 RAPD多态性分析:从选出的 63个RAPD图谱发现, 10株红曲菌指纹图谱条带基本一致,说明其遗传背景有很大相似性,但个别谱带之间存在不同程度差异,说明不同红曲分离株间又有丰富的遗传多样性。统计记录电泳结果,获得344条电泳条带的0?1矩阵。用NTSYS?PC?2.1计算10株红曲分离株遗传同一性和遗传差异性见表1,红曲分离株间同一性为36.05~86.05%,平均73.32%。聚类分析结果见图2,其中AS3.544与B、S与ZW-5的亲缘关系较近,尤其是AS3.972与古田同一性高达86.05%,遗传距离非常接近,它们可能有共同祖先。F处于相对独立的一支,与其它红曲菌亲缘关系均较远。
图1 引物S2042在10个红曲菌株中的RAPD扩增结果(略)
M:Marker;1:AS;3.554;2:AS 3.972;3:B;4:F;5:J;6:M-2;7:P;8:S;9:ZW-5;10:古田
图2 红曲分离株的系统聚类进化树(略)
表1 红曲分离株的同源性(左下)和差异性(右上)(略)
3 讨论
本研究显示虽然10株红曲菌来源各异,但同一性平均高达73.32%,说明其遗传背景有很大相似性,这与邢旺兴等[9]的结果一致。结合形态学特征发现RAPD遗传分析结果与菌株间的形态差异相关,如:RAPD多态性提示F 与其它红曲菌同一性仅有40%左右,多态性较高,很可能与种间差异有关,菌落形态和显微镜检表明F属M.ruber种而AS 3.554、B等则属M.anka种。这表明RAPD指纹图谱能较好地反映红曲菌株间的遗传关系,鉴别能力较强。均分离自福建的AS3.972和古田有地理距离优先聚类倾向,同一性高达86.05%,遗传距离非常近,表明地缘关系也是系统分类、遗传进化重要影响因子。
本研究利用分子生物学和数值分类方法研究红曲菌种质资源,从分子水平揭示红曲菌遗传背景差异,其结果与传统分类结果基本一致,表明RAPD分析具有较强菌株鉴别能力,不仅可作为一种辅助鉴别工具提高鉴定的准确性和客观性,而且为进一步研究红曲种质起源和进化提供。
【参考】
[1] Xing Wang?xing, Cheng Rong?zhen, Mi He?ming ,et al. Study on the physiological characteristics of seven ordinary Monascus[J]. The Journal of Pharmaceutical Practice,2001,19(4):231?233.
[2] 邢旺兴. 中药红曲基原真菌的高效毛细管电泳色谱法鉴别[J]. 第二军医大学学报,2000, 21(1):59?61.
[3] 邢旺兴,陈士景,宓鹤鸣,等. 中药红曲的薄层色谱法鉴别[J].药学实践杂志,2000,18(2):93?95.
[4] 邢旺兴,宓鹤鸣,陈斌,等. 气相色谱-模糊聚类分析法用于红曲基原菌的鉴别[J]. 中药杂志,2000, 25(6):329?334.
[5] 李钟庆,郭芳. 红曲菌的形态与分类学[M]. 北京:中国轻出版社,2003.
[6] 吴学谦,李海波,魏海龙,等. DNA分子标记技术在食用菌研究中的应用及进展[J].浙江林业科技, 2004,24(2):75?80.
[7] Weilliams JGK,Kubelik AR.DNA polymorphism amplified by arbitrary primers are useful as genetic markers[J].Nucleic Acids Res,1990,18(22):6531.
[8] 杨华,李联泰. 食用菌DNA提取方法研究[J]. 中国食用菌,2002,22(1):19?22.
[9] 邢旺兴,宓鹤鸣,陈士景,等.不同产地红曲基原菌的RAPD分析[J].药学实践杂志,2001,19(3):163?165.